Nat Med | یک رویکرد چند اُمیکس برای نقشهبرداری از چشمانداز یکپارچه تومور، ایمنی و میکروبی سرطان کولورکتال، تعامل میکروبیوم با سیستم ایمنی را آشکار میکند.
اگرچه نشانگرهای زیستی برای سرطان اولیه روده بزرگ در سالهای اخیر به طور گسترده مورد مطالعه قرار گرفتهاند، دستورالعملهای بالینی فعلی فقط بر مرحلهبندی تومور-غدد لنفاوی-متاستاز و تشخیص نقصهای ترمیم عدم تطابق DNA (MMR) یا ناپایداری ریزماهواره (MSI) (علاوه بر آزمایش استاندارد پاتولوژی) برای تعیین توصیههای درمانی متکی هستند. محققان عدم ارتباط بین پاسخهای ایمنی مبتنی بر بیان ژن، پروفایلهای میکروبی و استرومای تومور را در گروه سرطان روده بزرگ اطلس ژنوم سرطان (TCGA) و بقای بیمار مشاهده کردهاند.
با پیشرفت تحقیقات، گزارش شده است که ویژگیهای کمی سرطان اولیه کولورکتال، از جمله ماهیت سلولی، ایمنی، استرومایی یا میکروبی سرطان، به طور قابل توجهی با پیامدهای بالینی مرتبط هستند، اما هنوز درک محدودی از چگونگی تأثیر تعاملات آنها بر پیامدهای بیمار وجود دارد.
برای بررسی رابطه بین پیچیدگی فنوتیپی و پیامد، تیمی از محققان موسسه تحقیقات پزشکی سیدرا در قطر اخیراً یک امتیاز یکپارچه (mICRoScore) را توسعه داده و اعتبارسنجی کردهاند که گروهی از بیماران با میزان بقای خوب را با ترکیب ویژگیهای میکروبیوم و ثابتهای رد ایمنی (ICR) شناسایی میکند. این تیم یک تجزیه و تحلیل ژنومی جامع از نمونههای تازه منجمد شده از 348 بیمار مبتلا به سرطان کولورکتال اولیه، از جمله توالییابی RNA تومورها و بافت کولورکتال سالم منطبق، توالییابی کل اگزوم، گیرنده عمیق سلول T و توالییابی ژن rRNA باکتریایی 16S، و همچنین توالییابی کل ژنوم تومور برای توصیف بیشتر میکروبیوم، انجام داد. این مطالعه در مجله Nature Medicine با عنوان «اطلس یکپارچه تومور، ایمنی و میکروبیوم سرطان روده بزرگ» منتشر شد.

مقاله منتشر شده در مجله نیچر مدیسین
بررسی اجمالی AC-ICAM
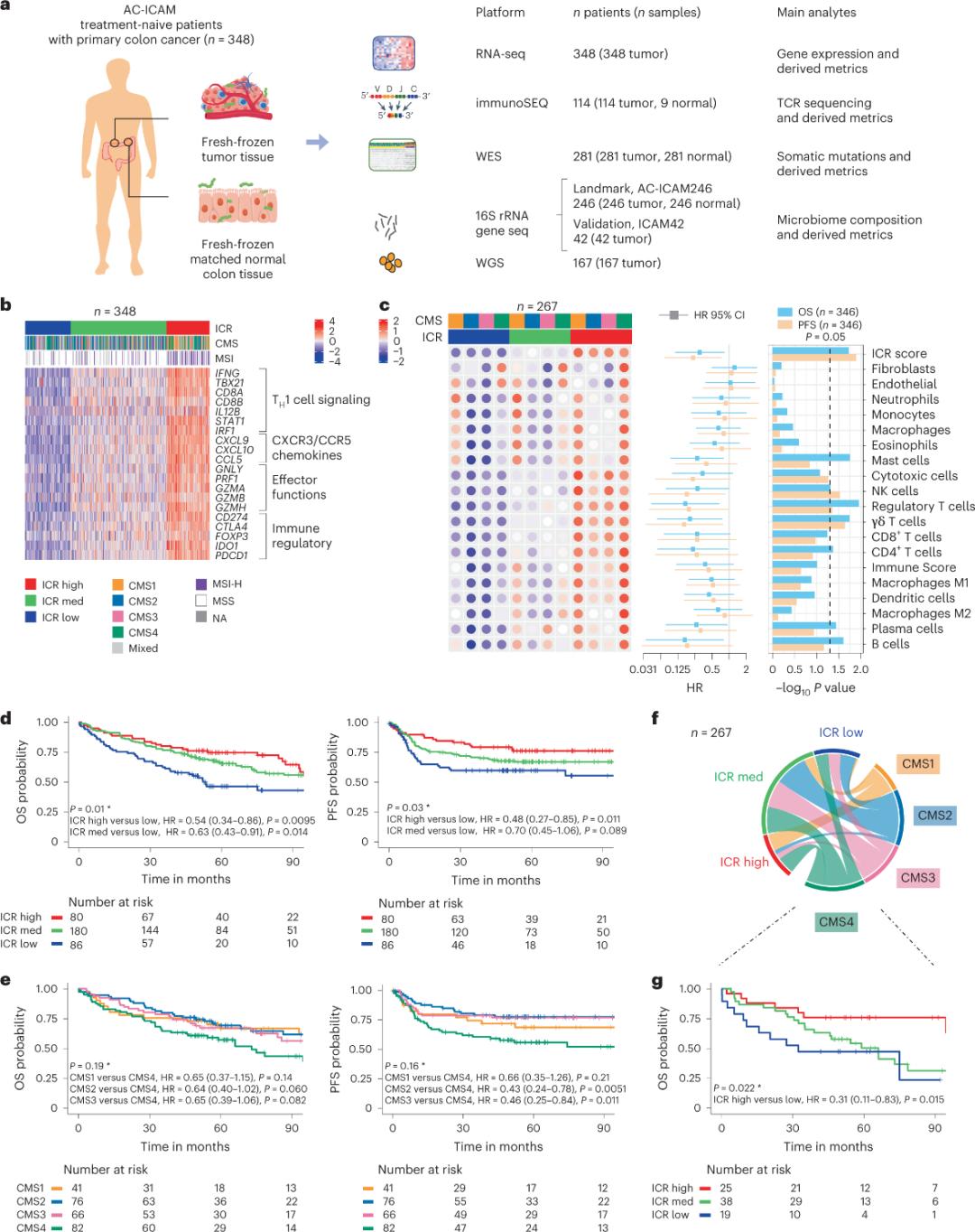
محققان از یک پلتفرم ژنومی متعامد برای تجزیه و تحلیل نمونههای تومور تازه منجمد شده و تطبیق بافت روده بزرگ سالم مجاور (جفتهای تومور-طبیعی) از بیمارانی با تشخیص بافتشناسی سرطان روده بزرگ بدون درمان سیستمیک استفاده کردند. بر اساس توالییابی کل اگزوم (WES)، کنترل کیفیت دادههای RNA-seq و غربالگری معیارهای ورود، دادههای ژنومی از 348 بیمار حفظ و برای تجزیه و تحلیلهای بعدی با میانگین پیگیری 4.6 سال استفاده شد. تیم تحقیقاتی این منبع را Sidra-LUMC AC-ICAM: نقشه و راهنمای تعاملات ایمنی-سرطان-میکروبیوم نامگذاری کرد (شکل 1).
طبقهبندی مولکولی با استفاده از ICR
تیم تحقیقاتی با جمعآوری مجموعهای مدولار از نشانگرهای ژنتیکی ایمنی برای نظارت مداوم بر ایمنی سرطان، به نام ثابت ایمنی رد (ICR)، ICR را با فشردهسازی آن در یک پنل 20 ژنی که انواع مختلف سرطان، از جمله ملانوما، سرطان مثانه و سرطان سینه را پوشش میدهد، بهینه کردند. ICR همچنین با پاسخ ایمونوتراپی در انواع مختلف سرطان، از جمله سرطان سینه، مرتبط بوده است.
ابتدا، محققان امضای ICR گروه AC-ICAM را با استفاده از یک رویکرد طبقهبندی مشترک مبتنی بر ژن ICR برای طبقهبندی این گروه به سه خوشه/زیرگروه ایمنی: ICR بالا (تومورهای داغ)، ICR متوسط و ICR پایین (تومورهای سرد) تأیید کردند (شکل 1b). محققان تمایل ایمنی مرتبط با زیرگروههای مولکولی اجماعی (CMS)، یک طبقهبندی مبتنی بر ترانسکریپتوم از سرطان روده بزرگ را مشخص کردند. دستههای CMS شامل CMS1/ایمنی، CMS2/کانونیکال، CMS3/متابولیک و CMS4/مزانشیمی بودند. تجزیه و تحلیل نشان داد که نمرات ICR با مسیرهای خاص سلولهای سرطانی در تمام زیرگروههای CMS همبستگی منفی دارند و همبستگی مثبت با مسیرهای سرکوبکننده سیستم ایمنی و مرتبط با استرومال فقط در تومورهای CMS4 مشاهده شد.
در تمام CMSها، فراوانی سلولهای کشنده طبیعی (NK) و زیرمجموعههای سلولهای T در زیرمجموعههای ایمنی بالای ICR بیشترین مقدار را داشت و تنوع بیشتری در سایر زیرمجموعههای لکوسیت وجود داشت (شکل 1c). زیرمجموعههای ایمنی ICR، OS و PFS متفاوتی داشتند و افزایش تدریجی ICR از پایین به بالا مشاهده شد (شکل 1d)، که نقش پیشآگهی ICR در سرطان کولورکتال را تأیید میکند.
شکل 1. طراحی مطالعه AC-ICAM، امضای ژنی مرتبط با سیستم ایمنی، زیرگروههای ایمنی و مولکولی و بقا.
ICR سلولهای T غنیشده با تومور و تکثیرشده به صورت کلونی را به دام میاندازد
گزارش شده است که تنها تعداد کمی از سلولهای T که به بافت تومور نفوذ میکنند، برای آنتیژنهای تومور اختصاصی هستند (کمتر از 10٪). بنابراین، اکثر سلولهای T درون توموری به عنوان سلولهای T ناظر (سلولهای T ناظر) شناخته میشوند. قویترین همبستگی با تعداد سلولهای T معمولی با TCRهای مولد در زیرجمعیتهای سلولهای استرومایی و لکوسیتی (که توسط RNA-seq شناسایی شدهاند) مشاهده شد که میتواند برای تخمین زیرجمعیتهای سلولهای T استفاده شود (شکل 2a). در خوشههای ICR (طبقهبندی کلی و CMS)، بالاترین کلونالیتی TCRهای SEQ ایمنی در گروههای ICR-high و زیرگروه CMS CMS1/immune (شکل 2c) مشاهده شد، که بیشترین نسبت تومورهای ICR-high را داشتند. با استفاده از کل رونوشت (18270 ژن)، شش ژن ICR (IFNG، STAT1، IRF1، CCL5، GZMA و CXCL10) در میان ده ژن برتر با کلونالیتی SEQ ایمنی TCR بودند (شکل 2d). کلونالیتی TCR ImmunoSEQ با اکثر ژنهای ICR همبستگی قویتری نسبت به همبستگیهای مشاهده شده با استفاده از نشانگرهای CD8+ پاسخدهنده به تومور داشت (شکل 2f و 2g). در نتیجه، تجزیه و تحلیل فوق نشان میدهد که امضای ICR وجود سلولهای T غنیشده با تومور و تکثیرشده به صورت کلونی را نشان میدهد و ممکن است پیامدهای پیشآگهی آن را توضیح دهد.
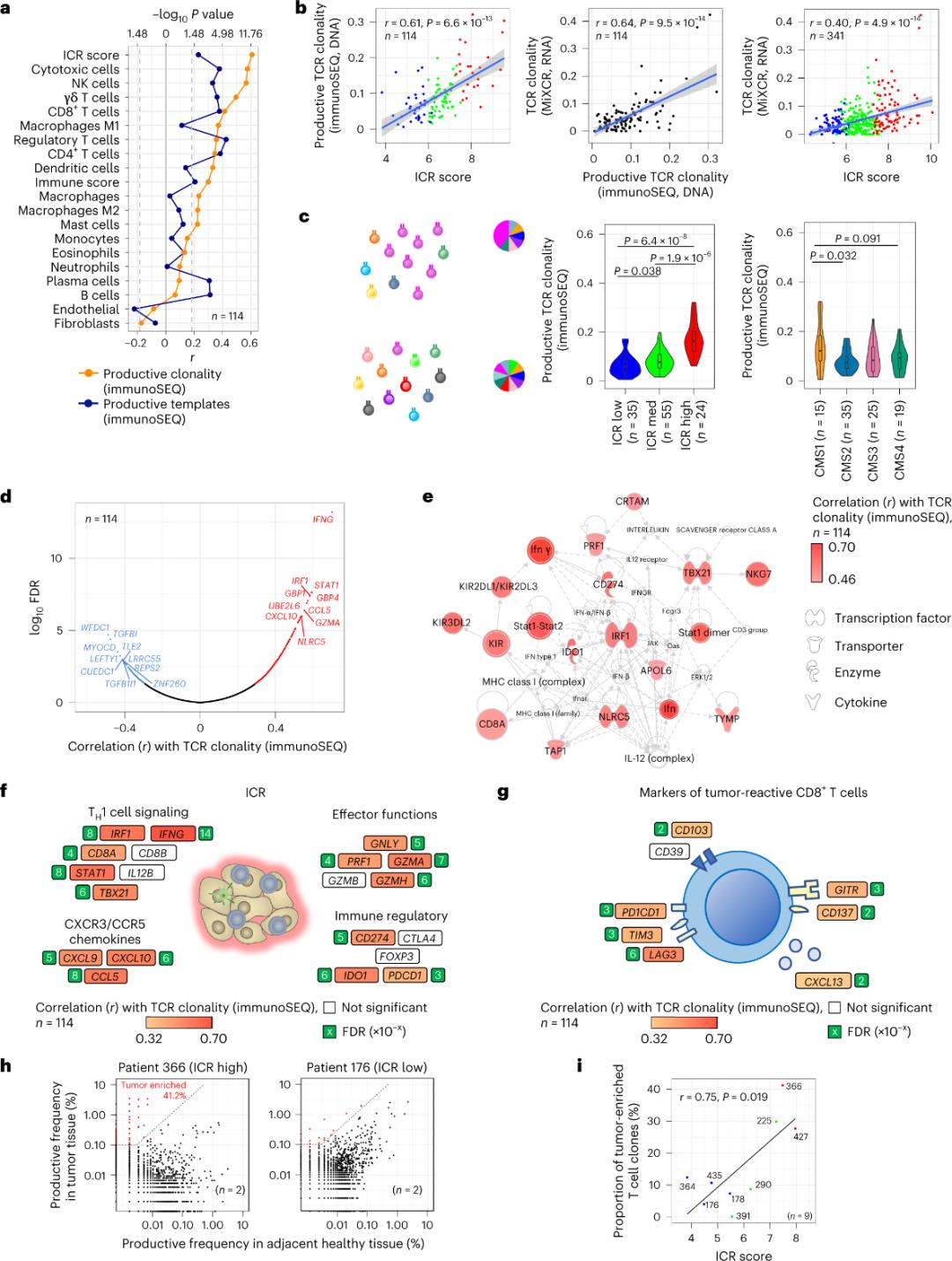
شکل 2. معیارهای TCR و همبستگی با ژنهای مرتبط با ایمنی، زیرگروههای ایمنی و مولکولی.
ترکیب میکروبیوم در بافتهای سالم و سرطانی روده بزرگ
محققان توالییابی rRNA 16S را با استفاده از DNA استخراجشده از بافت تومور و روده بزرگ سالم منطبق از 246 بیمار انجام دادند (شکل 3a). برای اعتبارسنجی، محققان علاوه بر این، دادههای توالییابی ژن rRNA 16S را از 42 نمونه تومور اضافی که DNA طبیعی منطبق برای تجزیه و تحلیل نداشتند، تجزیه و تحلیل کردند. ابتدا، محققان فراوانی نسبی فلور را بین تومورهای منطبق و بافت روده بزرگ سالم مقایسه کردند. کلستریدیوم پرفرنژنس در تومورها در مقایسه با نمونههای سالم به طور قابل توجهی افزایش یافته بود (شکل 3a-3d). تفاوت معنیداری در تنوع آلفا (تنوع و فراوانی گونهها در یک نمونه واحد) بین نمونههای تومور و سالم وجود نداشت و کاهش متوسطی در تنوع میکروبی در تومورهای با ICR بالا نسبت به تومورهای با ICR پایین مشاهده شد.
برای تشخیص ارتباطات بالینی مرتبط بین پروفایلهای میکروبی و پیامدهای بالینی، محققان قصد داشتند از دادههای توالییابی ژن 16S rRNA برای شناسایی ویژگیهای میکروبیومی که بقا را پیشبینی میکنند، استفاده کنند. در AC-ICAM246، محققان یک مدل رگرسیون OS Cox را اجرا کردند که 41 ویژگی با ضرایب غیر صفر (مرتبط با خطر مرگ و میر افتراقی) را انتخاب کرد که طبقهبندیکنندههای MBR نامیده میشوند (شکل 3f).
در این گروه آموزشی (ICAM246)، امتیاز MBR پایین (MBR<0، MBR پایین) با خطر مرگ به طور قابل توجهی پایینتر (85٪) همراه بود. محققان ارتباط بین MBR پایین (خطر) و بقای کلی طولانی مدت را در دو گروه مستقلاً معتبر (ICAM42 و TCGA-COAD) تأیید کردند. (شکل 3) این مطالعه همبستگی قوی بین کوکسیهای درون معدهای و امتیازات MBR را نشان داد که در بافت توموری و سالم روده بزرگ مشابه بودند.
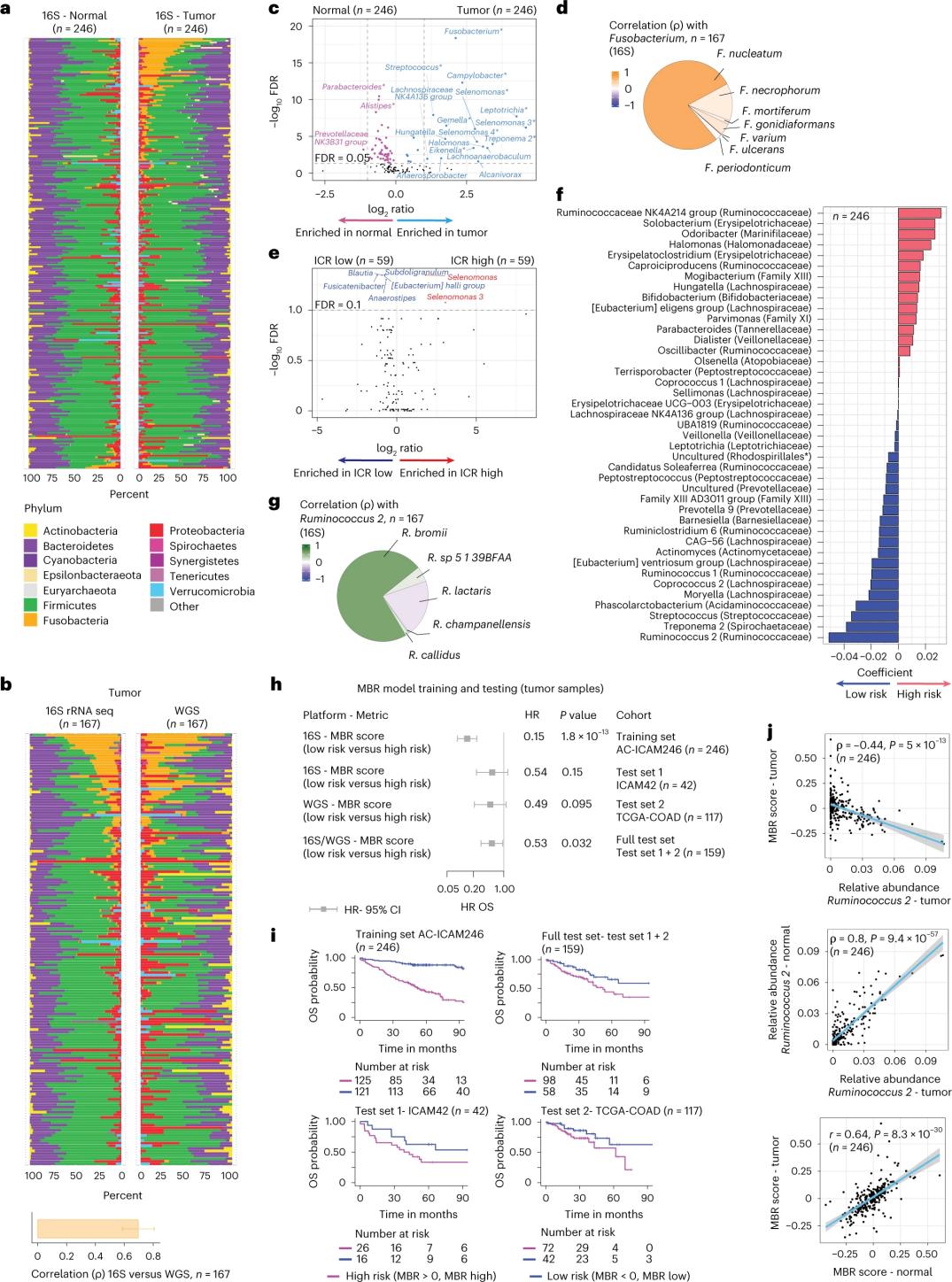
شکل ۳. میکروبیوم در بافتهای توموری و سالم و ارتباط آن با ICR و بقای بیمار.
نتیجهگیری
رویکرد چند-اومیکس مورد استفاده در این مطالعه، امکان تشخیص و تجزیه و تحلیل کامل امضای مولکولی پاسخ ایمنی در سرطان روده بزرگ را فراهم میکند و تعامل بین میکروبیوم و سیستم ایمنی را آشکار میسازد. توالییابی عمیق TCR بافتهای تومور و سالم نشان داد که اثر پیشآگهی ICR ممکن است به دلیل توانایی آن در به دام انداختن کلونهای سلول T غنی از تومور و احتمالاً آنتیژن اختصاصی تومور باشد.
با تجزیه و تحلیل ترکیب میکروبیوم تومور با استفاده از توالییابی ژن 16S rRNA در نمونههای AC-ICAM، این تیم یک امضای میکروبیوم (نمره خطر MBR) با ارزش پیشآگهی قوی شناسایی کرد. اگرچه این امضا از نمونههای تومور گرفته شده بود، اما همبستگی قوی بین کولورکتوم سالم و نمره خطر MBR تومور وجود داشت که نشان میدهد این امضا ممکن است ترکیب میکروبیوم روده بیماران را ثبت کند. با ترکیب نمرات ICR و MBR، شناسایی و اعتبارسنجی یک نشانگر زیستی دانشجویی چند اُمیک که بقای بیماران مبتلا به سرطان روده بزرگ را پیشبینی میکند، امکانپذیر شد. مجموعه دادههای چند اُمیک این مطالعه منبعی برای درک بهتر زیستشناسی سرطان روده بزرگ و کمک به کشف رویکردهای درمانی شخصیسازیشده فراهم میکند.
زمان ارسال: ۱۵ ژوئن ۲۰۲۳
 中文网站
中文网站